上海百趣生物科技有限公司
13 年
手机商铺
商家活跃:
产品热度:
- NaN
- 0.5
- 0.5
- 2.5
- 2.5
文献支持
短链脂肪酸高通量靶标代谢组学
询价
公司新闻/正文
代谢组学两种常见图形制作分享
1669 人阅读发布时间:2020-12-07 09:23
趣粉:小编,请问文献里面的美图是如何制作出来哒?比如韦恩图、箱形图等。
阿趣代谢公众号小编:呀,咱们可真是心有灵犀一点通呢,本期小编邀请到了 BIOTREE 的明星老师杜杰手把手教大家制作这两种图片呢。话不多说,赶快学起来吧!
1
韦恩图制作
分析网站链接:http://jvenn.toulouse.inra.fr/app/example.html
首先,进行网站,导入下图箭头所指相关案例数据。
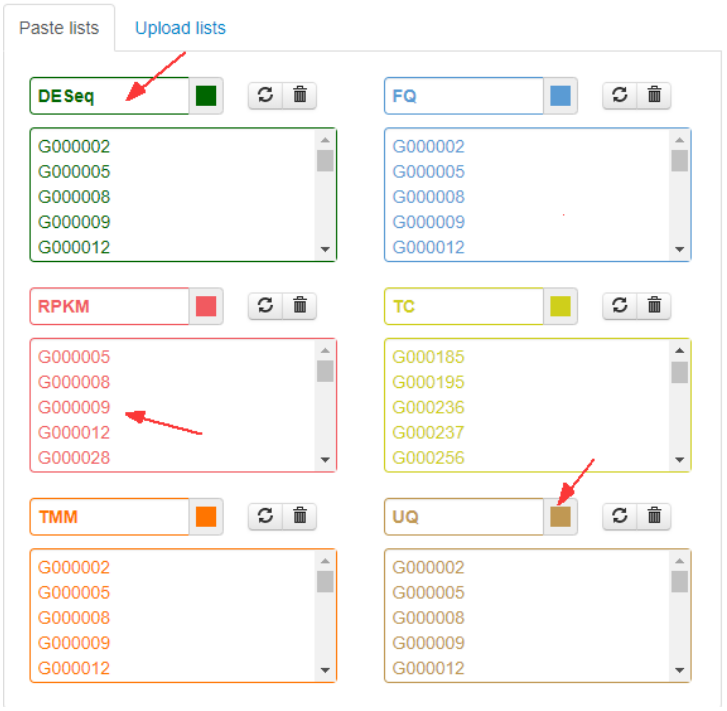
上图箭头所指均可自由编辑哦,这里显示输入了 6 组不同数据集(网站目前上限数据集为 6 组哦~)。友情提醒,如果是代谢组学数据,那一般只需导入代谢物质名称或编号就可以啦。
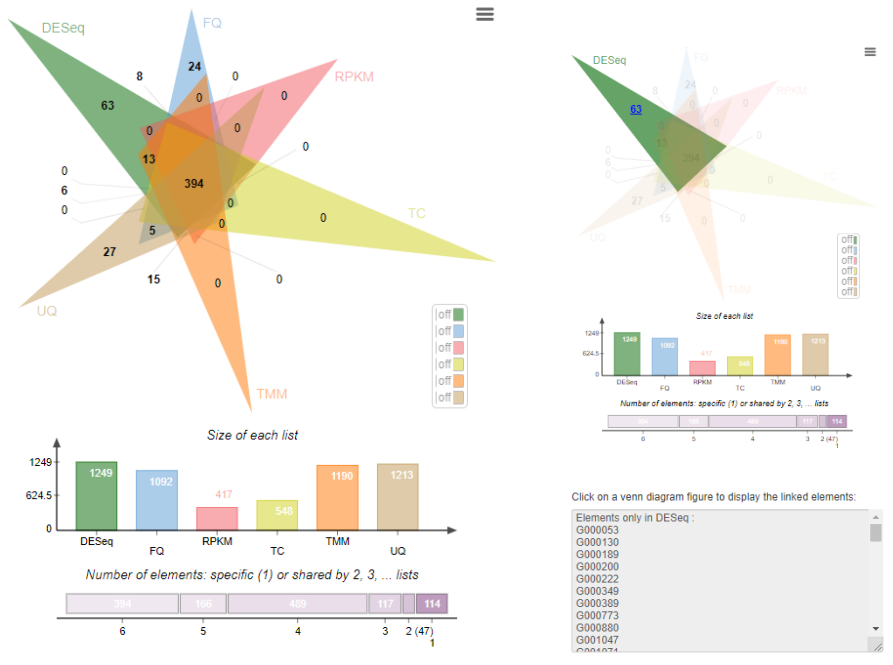
韦恩分析结果展示如上图(左),如需调出右图中的单组对应信息内容,则鼠标左键点击选中相应数字即可,不要太方便呀~
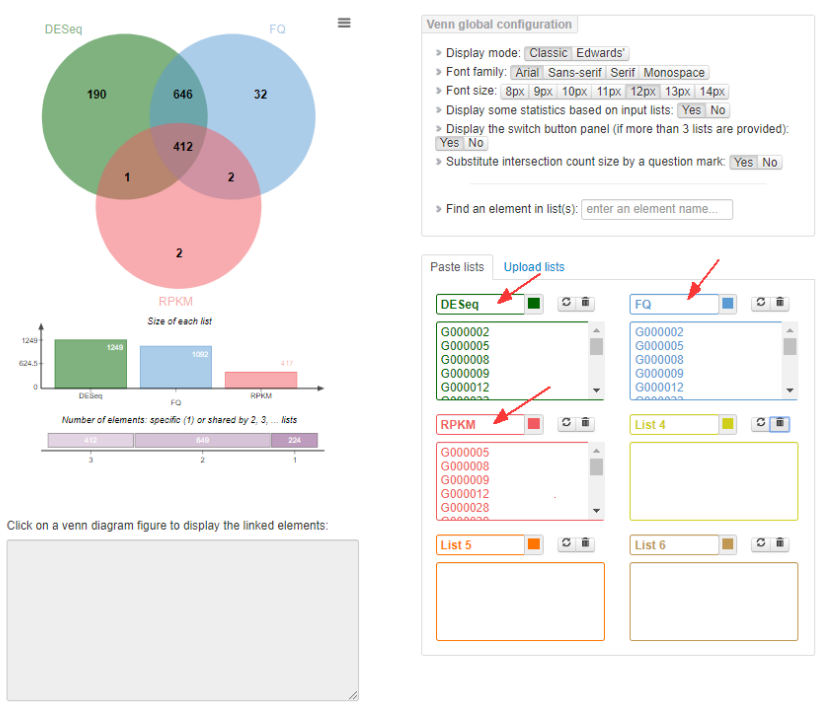
当然,如果只要三组数据集的韦恩图展示,那么,我们只需输入三个对应的 list 数据集就可以啦~,这不香嘛~
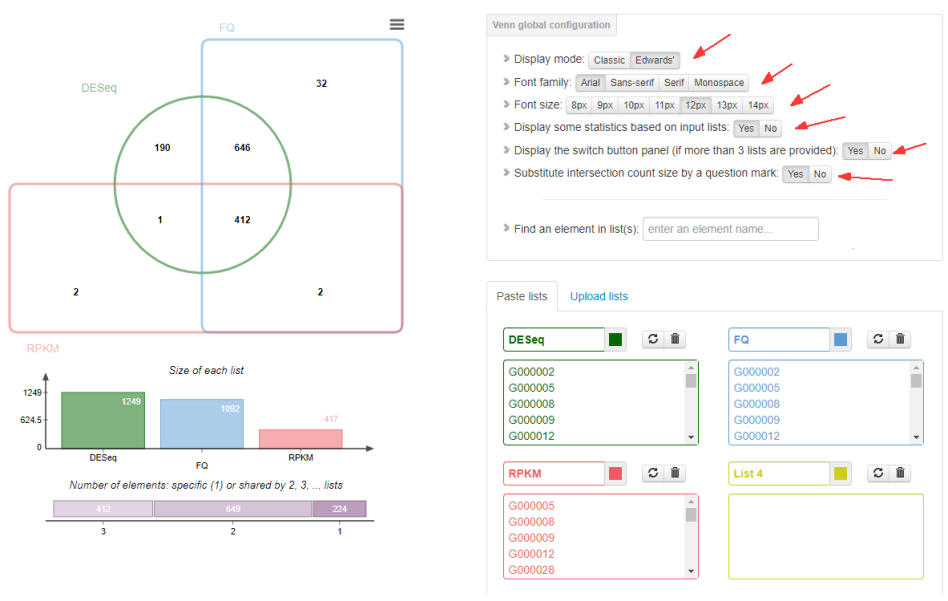
接下来,还可对图形进一步调整展示。比如:图形展现形式、图形字体类型、大小等,根据需求灵活调整就可以了。
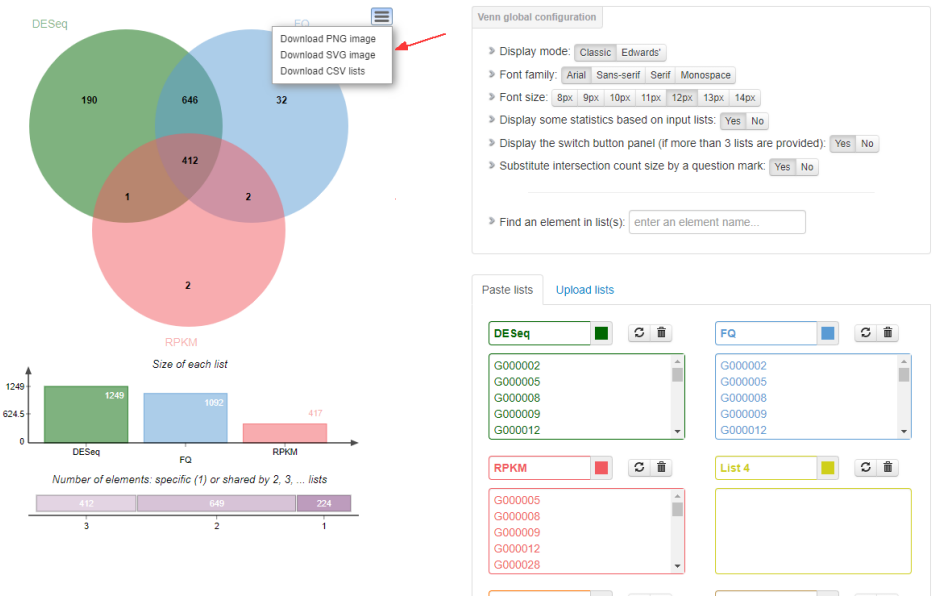
最后,调试好分析出来的图形和表格结果进行本地下载保存,可千万别忘了哦~
Tips:如果需要展示的数据集超过6组的话,咋办?给大家推荐一个数据集合可视化神包—UpSetR,感兴趣的小伙伴们可自行搜索查询~
分析代码包:ggplot2 & ggpubr
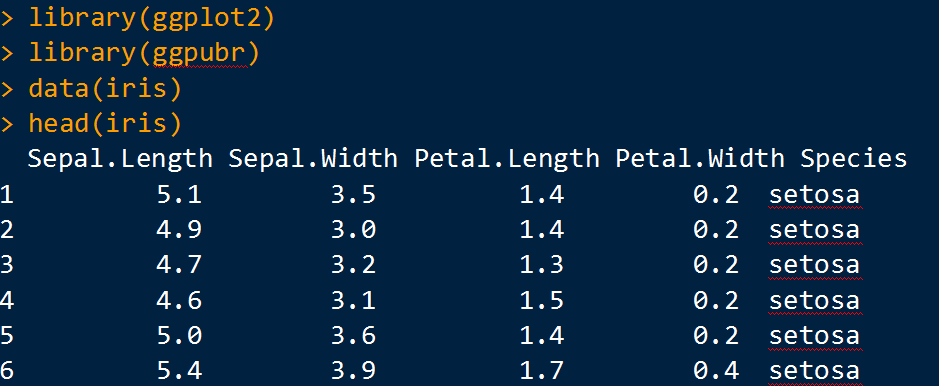
以iris 数据集为例,首先在 Rstudio 里载入 ggplot2 和 ggpubr 两个包(相关包安装教程可参考:http://www.bioconductor.org/install/),同时查看下 iris 数据集的表头信息,这里选取「Sepal.Length」作为关注变量来绘制不同组间箱线图含量表达展示。
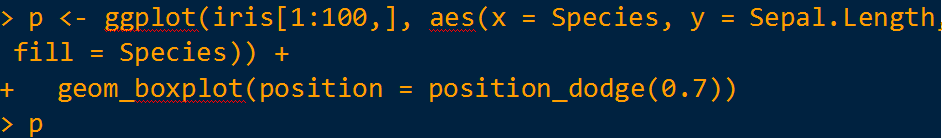
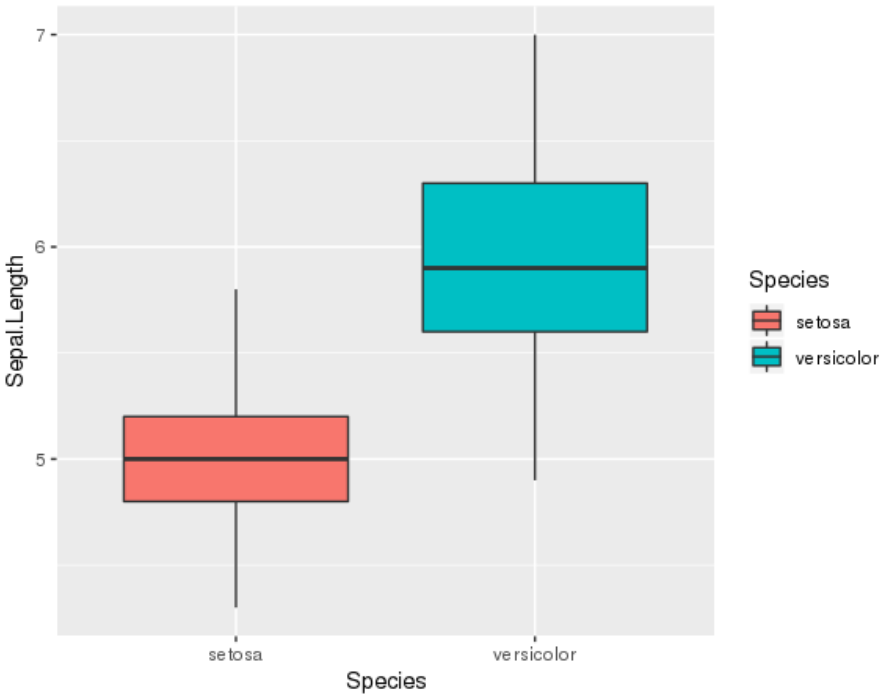
首先,绘制两组间的箱线图结果,如下图:
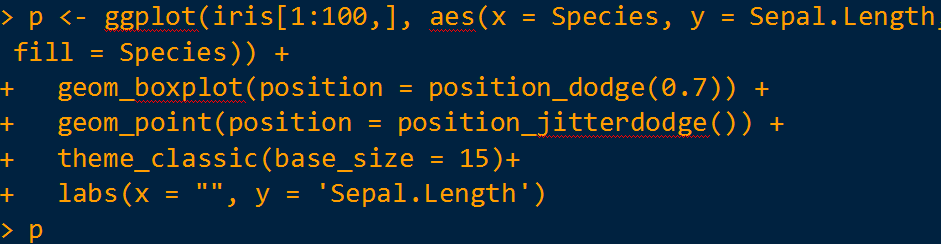
如果需要在图中显示不同的样本散点和横纵坐标标题,则代码添加如下:
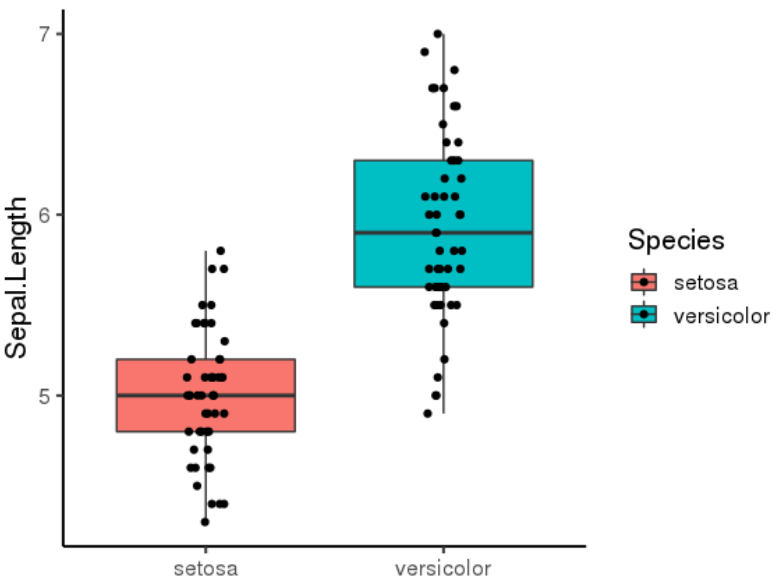
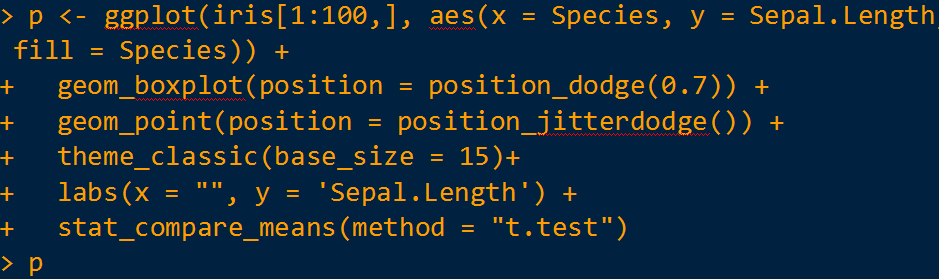
有时需要在两组间添加检验计算的 p 值,这里以 T 检验为例,则只需添加计算函数 stat_compare_means(method = "t.test")
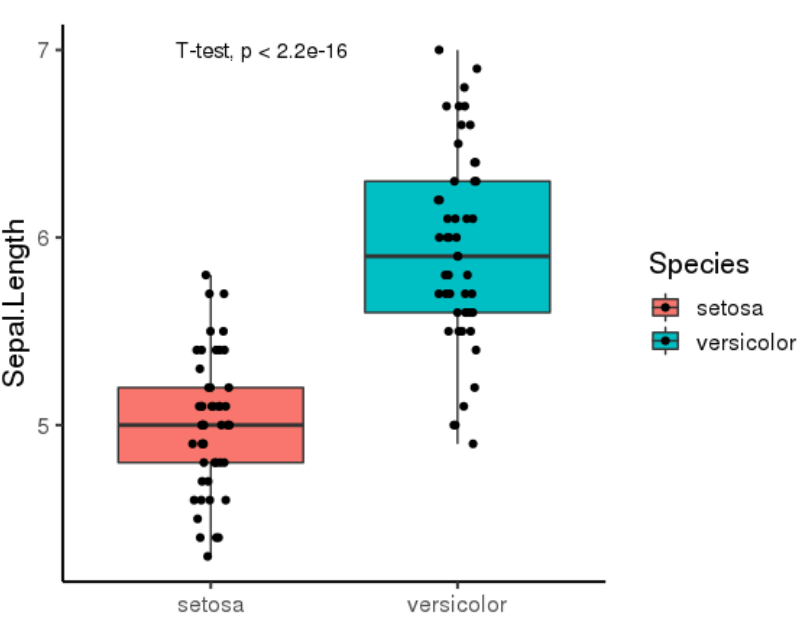
当然,如果要把 T 检验的方法调整成秩和检验,则
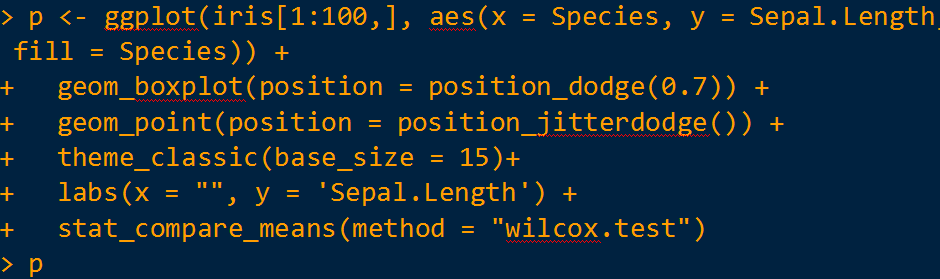
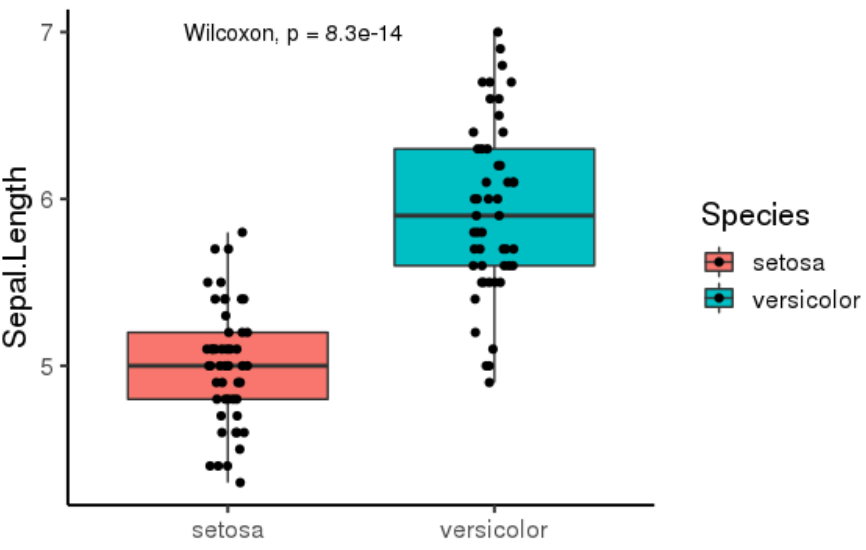
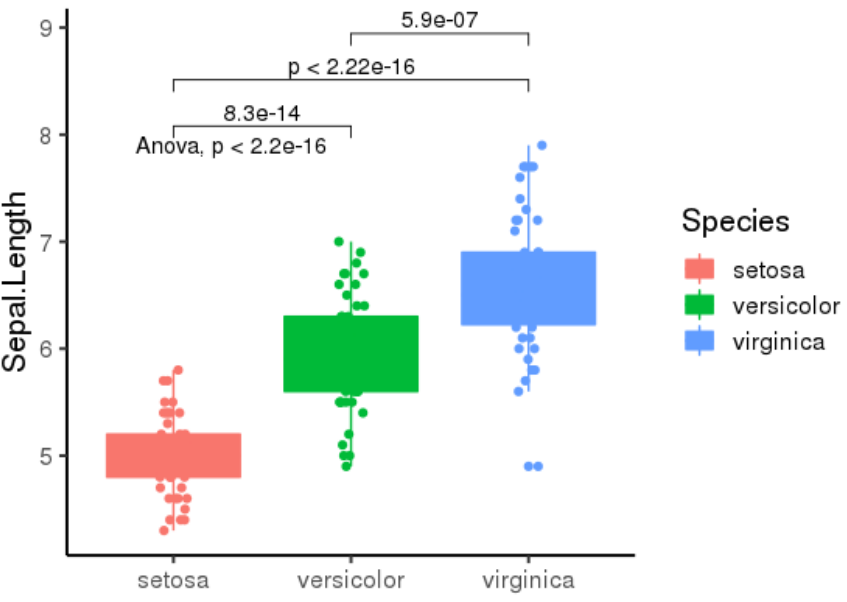
倘若需做三组(或三组以上)箱线图展示,同时加上 Kruskal-Wallis 多组检验结果及 post-hoc 两两比较结果,则
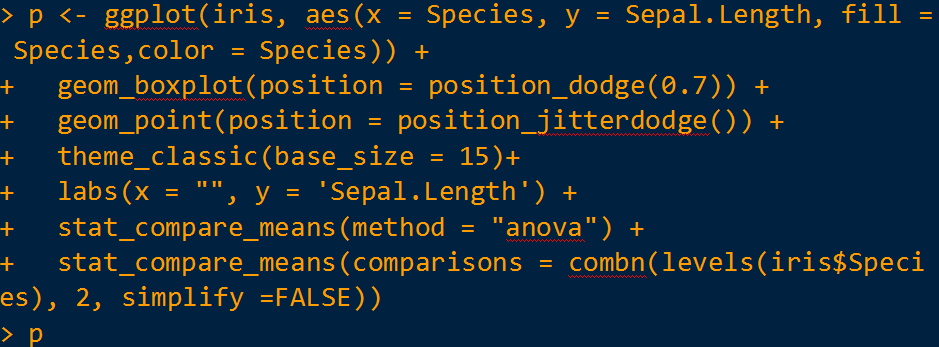
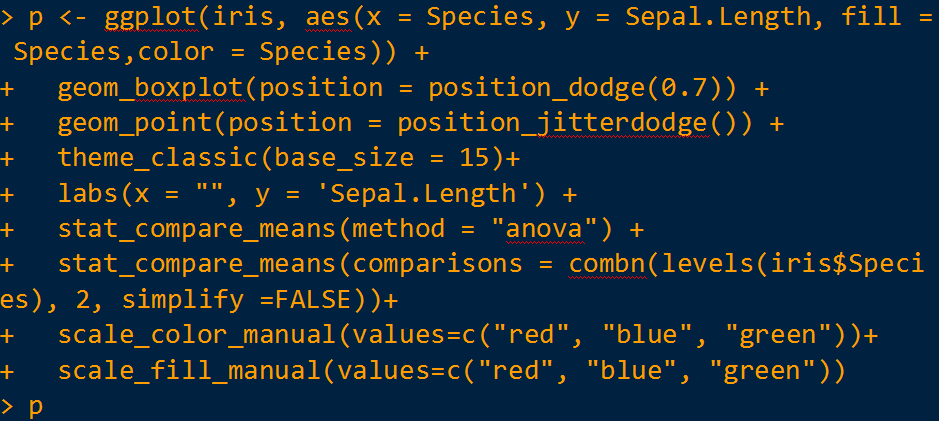
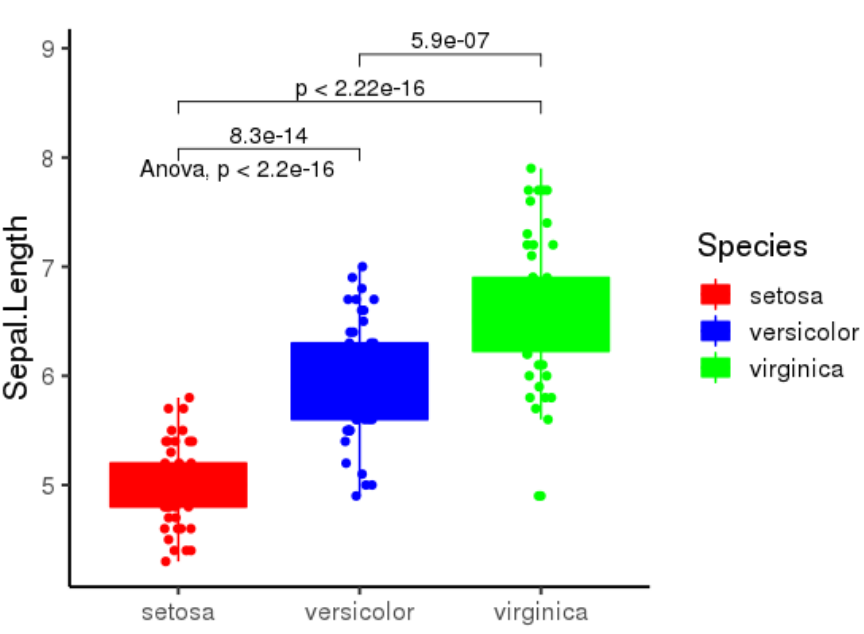
最后,每组的分组颜色如果要自由定义设置,那么代码调整如下:
教完收工~
如需代码可以在微信公众号后台留言:姓名+单位+手机+邮箱+代码。
阿趣代谢公众号小编:呀,咱们可真是心有灵犀一点通呢,本期小编邀请到了 BIOTREE 的明星老师杜杰手把手教大家制作这两种图片呢。话不多说,赶快学起来吧!
1
韦恩图制作
分析网站链接:http://jvenn.toulouse.inra.fr/app/example.html
首先,进行网站,导入下图箭头所指相关案例数据。


上图箭头所指均可自由编辑哦,这里显示输入了 6 组不同数据集(网站目前上限数据集为 6 组哦~)。友情提醒,如果是代谢组学数据,那一般只需导入代谢物质名称或编号就可以啦。

韦恩分析结果展示如上图(左),如需调出右图中的单组对应信息内容,则鼠标左键点击选中相应数字即可,不要太方便呀~

当然,如果只要三组数据集的韦恩图展示,那么,我们只需输入三个对应的 list 数据集就可以啦~,这不香嘛~

接下来,还可对图形进一步调整展示。比如:图形展现形式、图形字体类型、大小等,根据需求灵活调整就可以了。

最后,调试好分析出来的图形和表格结果进行本地下载保存,可千万别忘了哦~
Tips:如果需要展示的数据集超过6组的话,咋办?给大家推荐一个数据集合可视化神包—UpSetR,感兴趣的小伙伴们可自行搜索查询~
2
箱线图制作
箱线图制作
分析代码包:ggplot2 & ggpubr
以iris 数据集为例,首先在 Rstudio 里载入 ggplot2 和 ggpubr 两个包(相关包安装教程可参考:http://www.bioconductor.org/install/),同时查看下 iris 数据集的表头信息,这里选取「Sepal.Length」作为关注变量来绘制不同组间箱线图含量表达展示。

首先,绘制两组间的箱线图结果,如下图:




有时需要在两组间添加检验计算的 p 值,这里以 T 检验为例,则只需添加计算函数 stat_compare_means(method = "t.test")


当然,如果要把 T 检验的方法调整成秩和检验,则


倘若需做三组(或三组以上)箱线图展示,同时加上 Kruskal-Wallis 多组检验结果及 post-hoc 两两比较结果,则


最后,每组的分组颜色如果要自由定义设置,那么代码调整如下:


教完收工~
如需代码可以在微信公众号后台留言:姓名+单位+手机+邮箱+代码。






