上海百趣生物科技有限公司
13 年
手机商铺
商家活跃:
产品热度:
- NaN
- 0.7000000000000002
- 0.7000000000000002
- 2.7
- 2.7
修饰蛋白定性研究
询价
推荐产品
公司新闻/正文
小小代码造就精美绘图——“瀑布图”
394 人阅读发布时间:2022-08-04 11:47
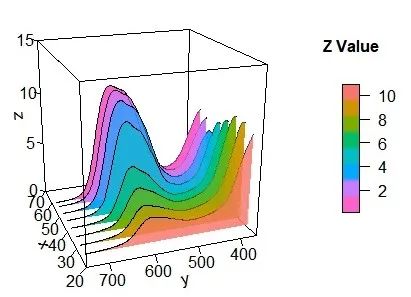
瀑布图是一种用于展示拥有相同的X轴变量数据、不同的Y轴离散型变量和Z轴数值变量的专业绘图,它可以清晰地展示不同样本对同一差异蛋白的变化关系。
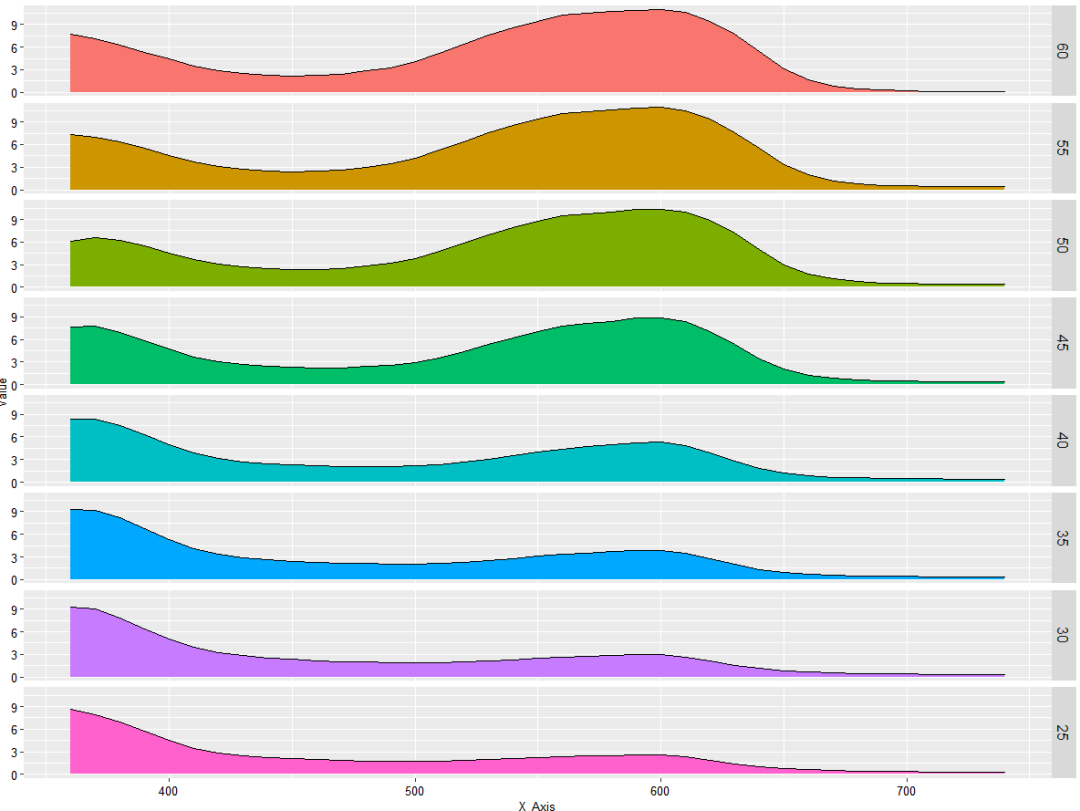
备注:X轴变量数据(如不同的指标)、不同的Y轴离散型变量(不同样本相对含量)
绘图步骤
一、载入R包
文件命名为Waterfall_Data.csv
data<-read.csv("Waterfall_data.csv",stringsAsFactors=FALSE)
三、整理数据
ggplot(plotdata,aes(X_Axis,value,fill=variable))+
调整颜色

备注:X轴变量数据(如不同的指标)、不同的Y轴离散型变量(不同样本相对含量)
需要用到的R包
一、ggplot2 绘图用R包
二、RColorBrewer 包含大量专业绘图色,绘制多样本图的基础
三、reshape2 用于整理数据的R包绘图步骤
一、载入R包
library(ggplot2)library(RColorBrewer)
library(reshape2)
二、导入数据
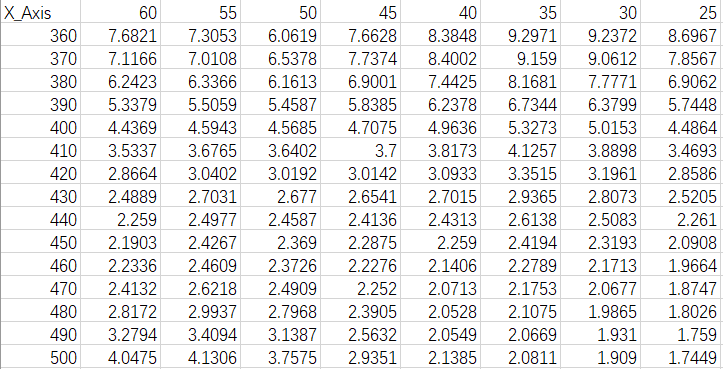
文件命名为Waterfall_Data.csv
data<-read.csv("Waterfall_data.csv",stringsAsFactors=FALSE)
三、整理数据
colnames(data)<-c("X_Axis",seq(60,25,-5))plotdata<-melt(data,id.vars = "X_Axis")
四、绘制瀑布图ggplot(plotdata,aes(X_Axis,value,fill=variable))+
geom_area(color="black",size=0.25)+facet_grid(variable~.)+theme(text=element_text(size=15,face="plain",color="black"),axis.title=element_text(size=10,face="plain",color="black"),axis.text = element_text(size=10,face="plain",color="black"),legend.position="none" )进阶画法(3D瀑布图) 相对于行分面瀑布图,3D瀑布图中不同类别间的差异更为直观,能更好地观察类与类之间的差距。 载入R包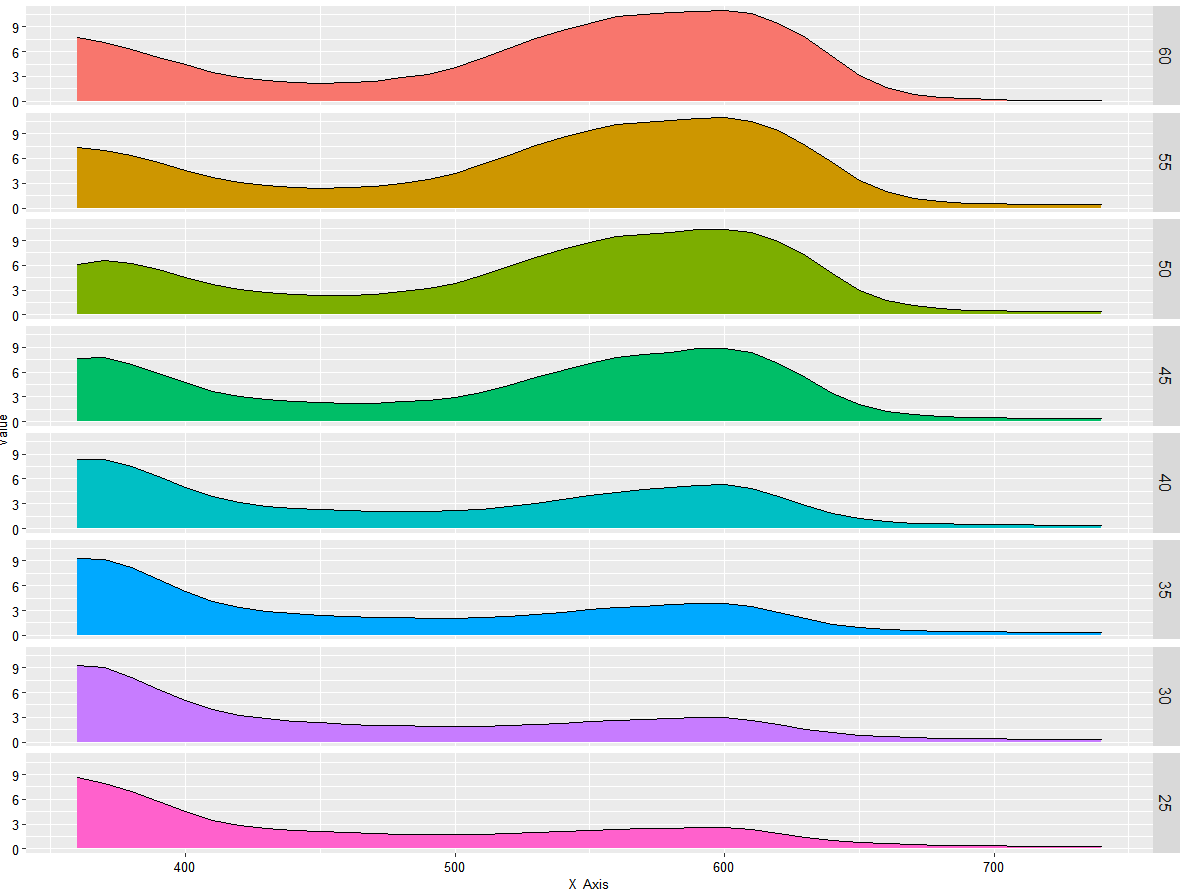
library(plot3D)library(RColorBrewer)导入数据 data<-read.csv("Facting_Data.csv",check.names =FALSE) 数据处理N<-ncol(data)-1plotdata<-data.frame(x=numeric(),y=numeric(),variable=character())for (i in 1:N){tempdata<-data.frame(spline(data[,1],data[,i+1],n=300,method= "natural"))tempdata$variable<-colnames(data)[i+1]plotdata<-rbind(plotdata,tempdata)}#插值处理plotdata$variable<-as.numeric(plotdata$variable)group<-unique(plotdata$variable)M<-length(group)
调整颜色
gg_color_hue <- function(n) {hues = seq(15, 375, length = n + 1)hcl(h = hues, l = 65, c = 100)[1:n]}colormap <- rev(gg_color_hue(M))#brewer.pal(M,'RdYlGn')绘制3D瀑布图
pmar <- par(mar = c(5.1, 4.1, 4.1, 6.1))perspbox(z=as.vector(0),#add=TRUE,xlim=c(20,70),ylim=c(360,750),zlim=c(0,15),ticktype = "detailed",bty = "f",box = TRUE,colkey = FALSE,theta = -110, phi = 20, d=3)for (i in 1:M){df0<-plotdata[plotdata$variable==group[i],]Ndf<-nrow(df0)df<-rbind(df0,c(df0$x[1],df0$y[Ndf],df0$variable[Ndf]))with(df,polygon3D(x=variable,y=x, z=y, alpha=0.6,col=colormap[i],lwd = 3,add=TRUE,colkey = FALSE))with(df0,lines3D(x=variable,y=x, z=y,lwd = 0.5,col="black",add=TRUE))}colkey (col=colormap,clim=range(plotdata$y),clab = "Z Value", add=TRUE, length=0.5,side = 4)#设置图例备注:X轴变量数据(不同样本)、不同的Y轴离散型变量(不同指标)、Z轴数值变量(指标相对含量)